Regulatorische Genomik und Evolution von Tumoren
- Funktionelle und Strukturelle Genomforschung

Prof. Dr. Duncan Odom
Group Leader
Das Labor von Dr. Odom untersucht, wie genetische Sequenzinformationen die DNA-Regulationslandschaft der Zelle und damit die Entwicklung des Krebsgenoms beeinflussen.
Bild: © dkfz.de
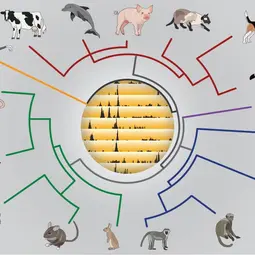
Bild: © dkfz.de
Unsere Forschung
Der Vergleich von Genomdaten verschiedener Arten hat gezeigt, dass das gewebespezifische Bindungsverhalten von Transkriptionsfaktoren, die Isolatoren, die Besetzung der Polymerase und die Enhancer-Aktivitäten während der Entwicklung des Organismus einem extensiven und schnellen Turn-Over unterliegen. Um zu demonstrieren, dass genetische Sequenzen die entscheidenden Faktoren für die Transkription und deren Regulation sind, hat das Odom-Labor ein Aneuploidie-Mausmodell des Down-Syndroms neu entworfen, das eine fast vollständige Kopie des menschlichen Chromosoms 21 trägt. Die funktionelle Analyse eines humanen Chromosoms im Kern einer Mauszelle lieferte einen starken Beweis dafür, dass cis-wirkende Sequenzen einen größeren Einfluss auf die Transkriptionsfaktor-Bindung, den Chromatin-Status und die Genexpression haben als trans-Einflüsse. Vor kurzem hat unsere Abteilung begonnen, die Einzelzell-RNA-Sequenzierung und die Sequenzierung des gesamten Genoms zu nutzen, um die molekulare Evolution zu verstehen. Jüngste hochkarätige Studien haben anhand einer Einzelzell-Transkriptionsanalyse schlüssig gezeigt, dass das Altern zu einer erheblichen Steigerung der Transkriptions-Variabilität von Zelle zu Zelle führt. Außerdem wurde im großen Maßstab analysiert, wie genetische und epigenetische Unterschiede zwischen Allelen die Mutagenese von Krebszellen verändern können.
Unsere laufende Arbeit konzentriert sich auf drei Hauptbereiche. Zunächst untersuchen wir weiter, wie genetische Sequenzvariationen die Genomregulation und Genexpression in normalen Körpergeweben beeinflussen, indem wir Beispiele aus nahe verwandten und entfernt voneinander verwandten Säugetieren vergleichen. Wir entwickeln neue Ansätze, die kürzlich entwickelte Single-Cell-Transkriptions- und Epigenom-Methoden sowie kontrollierte CTCF-Störungen (durch einen ERC Advanced Grant finanziert) nutzen. Zweitens erzeugen wir durch chemische Karzinogenese Lebertumoren in mehreren verschiedenen Säugetiermodellen und analysieren diese. Dies ist unseres Wissens die erste groß angelegte Herangehensweise zur Erzeugung sorgfältig kontrollierter Tumorkohorten, die zuverlässig und quantitativ verglichen werden können, um die zugrunde liegenden Prinzipien der Evolution des Krebsgenoms aufzuzeigen. Drittens testen wir, wie das Altern bei der Ausprägung der Genomstabilität mit der genetischen Diversität interagiert, dazu benutzen wir nahe verwandte Mäusearten mit einem ähnlichen Phänotyp auf Ebene des Organismus, jedoch mit stark voneinander abweichenden Genomen. Diese wissenschaftlichen Themen bieten einen großen Spielraum, um bestimmte Projekte an die wissenschaftlichen Interessen von künftigen-Doktoranden und Postdocs anzupassen.
Unser Team
- Profil anzeigen

Prof. Dr. Duncan Odom
Group Leader
- Profil anzeigen

Dr. Paul Ginno
Staff Scientist
- Profil anzeigen

Dr. Stefania Del Prete
PostDoc
- Profil anzeigen

Dr. James Cleland
PostDoc
- Profil anzeigen

Dr. Veronica Busa
PostDoc
- Profil anzeigen
Dr. Jusung Lee
PostDoc
- Profil anzeigen

Dr. Raphael Teodoro Franciscani Coimbra
Bioinformatician
- Profil anzeigen

Anja Schneider
Lab Manager
- Profil anzeigen

Marie-Luise Koch
Lab Manager
- Profil anzeigen
Nina Wilhelm
Lab Technician
- Profil anzeigen

Lilla Pecori
Secretary
- Profil anzeigen
Eileen Haage
Secretary
- Profil anzeigen

Milica Bekavac
PhD Student
- Profil anzeigen

Eleonore Boiral
PhD Student
- Profil anzeigen
Michele Framarin
PhD Student
- Profil anzeigen

Irem Tellioglu Akcay
PhD Student
- Profil anzeigen

Lea Christine Wölbert
PhD Student
Freunde aus anderen Laboren
- Profil anzeigen

Dr. Ivana Winkler
PostDoc
- Profil anzeigen

Francesca Coraggio
Lab Manager
- Profil anzeigen

Perrine Lacour
PhD Student
- Profil anzeigen

Anna Mathioudaki
PostDoc
- Profil anzeigen

Domenico Calafato
PhD Student
- Profil anzeigen

Heng Luo
PhD Student
-

Fritz Donald Hansen
Alumni
Ausgewählte Publikationen
Milica Bekavac, Raphael Coimbra, Veronica F Busa, Mikaela Behm, Rebecca E Wagner, Angela Goncalves, Sabine Begall, Michaela Frye, Duncan T Odom
Klaudija Daugelaite, Perrine Lacour, Ivana Winkler, Marie-Luise Koch, Anja Schneider, Nina Schneider, Francesca Coraggio, Alexander Tolkachov, Xuan Phuoc Nguyen, Adriana Vilkaite, Julia Rehnitz, Duncan T Odom, Angela Goncalves
Panten, J.* ; Del Prete, S. *; Cleland, J. ; Saunders, L. M.* ; van Riet, J.* ; Schneider, A.* ; Ginno, P.* ; Schneider, N.* ; Koch, M.-L.* ; Chen, X. ; Gerstung, M.* ; Stegle, O.* ; Arnold, A. P. ; Turner, J. M. A. ; Heard, E. ; Odom, D.*
Winkler, I.* ; Tolkachov, A.* ; Lammers, F.* ; Lacour, P.* ; Daugelaite, K.* ; Schneider, N.* ; Koch, M.-L.* ; Panten, J.* ; Grünschläger, F.* ; Poth, T. ; Ávila, B. M. d. ; Schneider, A. ; Haas, S.* ; Odom, D. T.* ; Gonçalves, Â.*
Anderson, C. J. ; Talmane, L. ; Ginno, P. A.*; Semple, C. A. ; Odom, D.* ; Aitken, S. J. ; Taylor, M. S.; et al.
Ginno, P. ; Borgers, H.* ; Ernst, C. ; Schneider, A.* ; Behm, M.* ; Aitken, S. J. ; Taylor, M. S. ; Odom, D. *
Kontaktieren Sie uns

Prof. Dr. Duncan Odom
Group LeaderPostanschrift:

